अमेरिकन विद्वान एरिक एस. लँडर यांनी 1996 मध्ये औपचारिकपणे सिंगल न्यूक्लियोटाइड पॉलिमॉर्फिझम (SNP) तिसऱ्या पिढीचे आण्विक चिन्हक म्हणून प्रस्तावित केल्यानंतर, SNP चा मोठ्या प्रमाणावर आर्थिक गुणधर्म असोसिएशन विश्लेषण, जैविक अनुवांशिक संबंध नकाशा बांधकाम आणि मानवी रोगजनक जनुक तपासणीमध्ये केला गेला., रोग जोखीम निदान आणि अंदाज, वैयक्तिक औषध तपासणी, आणि इतर जैविक आणि वैद्यकीय संशोधन क्षेत्रे.नगदी पीक प्रजनन क्षेत्रात, SNP शोधणे आवश्यक गुणधर्मांची लवकर निवड लक्षात येऊ शकते.या निवडीत उच्च अचूकतेची वैशिष्ट्ये आहेत आणि मॉर्फोलॉजी आणि पर्यावरणीय घटकांचा हस्तक्षेप प्रभावीपणे टाळता येतो, ज्यामुळे प्रजनन प्रक्रिया मोठ्या प्रमाणात कमी होते.म्हणून, SNP मूलभूत संशोधनाच्या क्षेत्रात मोठी भूमिका बजावते.
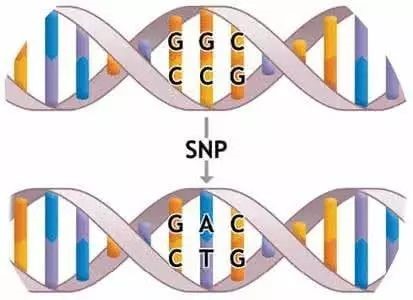
सिंगल न्यूक्लियोटाइड पॉलिमॉर्फिझम (सिंगल न्यूक्लियोटाइड पॉलिमॉर्फिझम, एसएनपी) या घटनेला सूचित करते की समान किंवा भिन्न प्रजातींच्या व्यक्तींच्या डीएनए अनुक्रमात एकाच स्थानावर एकल न्यूक्लियोटाइड फरक आहेत.एकाच बेसचे अंतर्भूत करणे, हटवणे, रूपांतरण आणि उलथापालथ यामुळे हा फरक होऊ शकतो.पूर्वी, एसएनपीची व्याख्या उत्परिवर्तनापेक्षा वेगळी होती.व्हेरिएंट लोकसला SNP लोकस म्हणून परिभाषित करण्यासाठी लोकसंख्येतील एका एलीलची वारंवारता 1% पेक्षा जास्त असणे आवश्यक आहे.तथापि, आधुनिक जैविक सिद्धांतांच्या विस्तारासह आणि तंत्रज्ञानाच्या वापरासह, SNP ची व्याख्या मर्यादित करण्यासाठी एलील वारंवारता यापुढे आवश्यक स्थिती नाही.नॅशनल सेंटर फॉर बायोटेक्नॉलॉजी इन्फॉर्मेशन (NCBI) अंतर्गत सिंगल न्यूक्लियोटाइड पॉलिमॉर्फिझम्स (dbSNP) डेटाबेसमध्ये समाविष्ट केलेल्या सिंगल न्यूक्लियोटाइड भिन्नता डेटानुसार, कमी-फ्रिक्वेंसी इन्सर्शन/डिलीशन, मायक्रोसेटेलाइट व्हेरिएशन इ. देखील समाविष्ट आहेत.
मानवी शरीरात, SNP ची वारंवारता 0.1% आहे.दुसऱ्या शब्दांत, प्रत्येक 1000 बेस जोड्यांमध्ये सरासरी एक SNP साइट आहे.घटनांची वारंवारता तुलनेने जास्त असली तरी, सर्व SNP साइट गुणांशी संबंधित उमेदवार चिन्हक असू शकत नाहीत.हे प्रामुख्याने SNP उद्भवलेल्या स्थानाशी संबंधित आहे.
सैद्धांतिकदृष्ट्या, एसएनपी जीनोम अनुक्रमात कुठेही येऊ शकते.कोडिंग प्रदेशात होणारे SNP समानार्थी उत्परिवर्तन आणि गैर-समानार्थी उत्परिवर्तन निर्माण करू शकतात, म्हणजेच, उत्परिवर्तनाच्या आधी आणि नंतर अमीनो आम्ल बदलते किंवा बदलत नाही.बदललेल्या अमिनो आम्लामुळे सामान्यतः पेप्टाइड साखळी त्याचे मूळ कार्य (मिससेन्स म्युटेशन) गमावते आणि भाषांतर रद्द (नॉनसेन्स म्यूटेशन) देखील होऊ शकते.नॉन-कोडिंग क्षेत्रांमध्ये आणि इंटरजेनिक प्रदेशांमध्ये उद्भवणारे SNPs mRNA स्प्लिसिंग, नॉन-कोडिंग RNA अनुक्रम रचना आणि ट्रान्सक्रिप्शन घटक आणि DNA च्या बंधनकारक कार्यक्षमतेवर परिणाम करू शकतात.विशिष्ट संबंध आकृतीमध्ये दर्शविला आहे:
SNP प्रकार:
अनेक सामान्य SNP टायपिंग पद्धती आणि त्यांची तुलना
वेगवेगळ्या तत्त्वांनुसार, सामान्य SNP शोध पद्धती खालील श्रेणींमध्ये विभागल्या जातात:
शोध पद्धतींची वर्गीकरण तुलना
टीप: टेबलमध्ये सूचीबद्ध सध्या अधिक सामान्य SNP शोध पद्धती वापरल्या जातात, विशिष्ट साइट हायब्रिडायझेशन (ASH), विशिष्ट साइट प्राइमर विस्तार (ASPE), सिंगल बेस एक्स्टेंशन (SBCE), विशिष्ट साइट कटिंग (ASC), जीन चिप तंत्रज्ञान, मास स्पेक्ट्रोमेट्री तंत्रज्ञान, इत्यादी इतर शोध पद्धतींचे वर्गीकरण आणि तुलना केलेली नाही.
वरील अनेक सामान्य SNP शोध पद्धतींमध्ये न्यूक्लिक अॅसिड शुद्धीकरणाची किंमत आणि वेळ अटळ आहे.तथापि, फोरजीनच्या डायरेक्ट पीसीआर तंत्रज्ञानावर आधारित संबंधित किट अशुद्ध नमुन्यांवर थेट पीसीआर किंवा क्यूपीसीआर प्रवर्धन करू शकतात, ज्यामुळे एसएनपी शोधण्यात अभूतपूर्व सोय होते.
फोरजीनची थेट PCR मालिका उत्पादने फक्त आणि अंदाजे नमुना शुद्धीकरण पायऱ्या वगळतात, ज्यामुळे टेम्पलेट्स तयार करण्यासाठी लागणारा वेळ आणि खर्च मोठ्या प्रमाणात कमी होतो.अद्वितीय Taq पॉलिमरेझमध्ये उत्कृष्ट प्रवर्धन क्षमता आहे आणि जटिल प्रवर्धन वातावरणातील विविध अवरोधकांना सहन करू शकते.ही वैशिष्ट्ये उच्च-उत्पन्न विशिष्ट उत्पादने मिळविण्यासाठी तांत्रिक हमी देतात. विविध नमुना प्रकारांसाठी फॉरजीन डायरेक्ट PCR/qPCR किट, जसे की: प्राण्यांच्या ऊती (उंदराची शेपटी, झेब्राफिश, इ.), वनस्पतीची पाने, बिया (पॉलीसेकेराइड्स आणि पॉलिफेनॉल नमुन्यांसह) इ.
पोस्ट वेळ: जुलै-23-2021